Luigi Ricciardi 1 , Rosa Mazzeo 2,*©, Angelo Raffaele Marcotrigiano 1 , Guglielmo Rainaldi 3 , Paolo Iovieno 4 , Vito Zonno 1 , Stefano Pavan 1 © and Concetta Lotti 2,*
- 1 Department of Soil, Plant and Food Sciences, Plant Genetics and Breeding Unit University of Bari, Via Amendola 165/A, 70125 Bari, Italy; luigi.ricciardi@uniba.it (Chwith i'r chwith);angelo.marcotrigiano@uniba.it (ARM); vito.zonno@uniba.it (VZ); stefano.pavan@uniba.it (SP)
- 2 Adran y Gwyddorau Amaethyddiaeth, Bwyd a'r Amgylchedd, Prifysgol Foggia, Via Napoli 25, 71122 Foggia, yr Eidal
- 3 Adran y Biowyddorau, Biotechnolegau a Biofferyllol, Prifysgol Bari, Via Orabona 4, 70125 Bari, yr Eidal; guglielmo.rainaldi@uniba.it
- 4 Department of Energy Technologies, Bioenergy, Biorefinery and Green Chemistry Division, ENEA Trisaia Research Center, S.S. 106 Ionica, km 419+500, 75026 Rotondella (MT), Italy; paolo.iovieno@enea.it
* Gohebiaeth: rosa.mazzeo@unifg.it (R.M.); concetta.lotti@unifg.it (C.L.)
Crynodeb:
Onion (Allium cepa L.) is the second most important vegetable crop worldwide and is widely appreciated for its health benefits. Despite its significant economic importance and its value as functional food, onion has been poorly investigated with respect to its genetic diversity. Herein, we surveyed the genetic variation in the “Acquaviva red onion” (ARO), a landrace with a century-old history of cultivation in a small town in the province of Bari (Apulia, Southern of Italy). A set of 11 microsatellite markers were used to explore the genetic variation in a germplasm collection consisting of 13 ARO populations and three common commercial types. Analyses of genetic structure with parametric and non-parametric methods highlighted that the ARO represents a well-defined gene pool, clearly distinct from the Tropea and Montoro landraces with which it is often mistaken. In order to provide a description of bulbs, usually used for fresh consumption, soluble solid content and pungency were evaluated, showing higher sweetness in the ARO with respect to the two above mentioned landraces. Overall, the present study is useful for the future valorization of the ARO, which could be promoted through quality labels which could contribute to limit commercial frauds and improve the income of smallholders.
Cyflwyniad
Mae'r genws Allium yn cynnwys tua 750 o rywogaethau [1], ymhlith y mae winwnsyn (Allium cepa L., 2n = 2x = 16) yn un o'r rhai mwyaf cyffredin. Mae gan A. cepa gylchred bob dwy flynedd ac mae'n croesi ymddygiad atgenhedlu. Y dyddiau hyn, mae cynhyrchu winwnsyn byd-eang (97.9 Mt) yn ei wneud yr ail gnwd llysiau pwysicaf ar ôl tomato [2]. Ers yr hen amser, mae bylbiau nionyn wedi'u defnyddio fel bwyd ac mewn cymwysiadau meddyginiaethol gwerin. Yn wir, adroddodd yr hen Eifftiaid eisoes nifer o fformiwlâu therapiwtig yn seiliedig ar y defnydd o garlleg a winwns mewn papyrws meddygol o'r 1550 CC, y Codex Ebers [3].
This versatile and healthy vegetable is consumed raw, fresh, or as processed product, and used to enhance the taste of many dishes. Several recent studies claim that onion consumption may reduce risk of cardiovascular diseases [4,5], obesity [6], diabetes [7], and various forms of cancer [8–10]. Onion health proprieties are often attributed to high levels of two classes of nutraceutical compounds: flavonoids and alk(en)yl cysteine sulphoxides (ACSOs). The first class includes flavonols and anthocyanins. Quercetin is the main detectable flavonol, known for its strong antioxidant and anti-inflammatory properties in free radical scavenging and transition metal ions binding [11]; whereas anthocyanins confer red/purple color to some onion varieties. As for ACSOs, the most abundant is isoalliin [(+)-trans-S-1-propenyl-L-cysteine sulfoxide] [12], a non-volatile and non-proteinogenic sulfur amino acid stored in the cells, which is indirectly responsible for the pungent aroma and taste of onions [13]. Ar ôl tarfu ar feinwe, mae isoalliin yn cael ei hollti gan yr ensym alliinase i gynhyrchu cyfres o gyfansoddion anweddol (pyrwfad, amonia, thiosylffonadau a S-ocsid propanethaidd) sy'n achosi rhwygo ac yn achosi arogl annymunol (plymio) [14]. The onion pungency is often measured as the amount, per gram of fresh weight, of pyruvic acid generated by hydrolysis [15,16].
Yn y gwledydd y basn Môr y Canoldir, a gynigir fel un o'r canolfannau amrywiaeth eilaidd o A. cepa [17,18], onion bulbs display a wide variability in shape, size, color, dry matter, and pungency [19-un]. Ar ben hynny, gall ffrwythloni sy'n seiliedig ar sylffwr, arferion agronomig, math o bridd, amodau hinsoddol, a genoteip cyltifarau neu dirluniau ddylanwadu ar ansawdd bwlb trwy roi gwerthoedd organoleptig a maethol rhyfedd. [23-un]. Yn yr Eidal, er gwaethaf yr argaeledd eang o germplasm winwns, dim ond ychydig o fathau o winwnsyn sy'n aml yn destun astudiaethau gwyddonol ac wedi'u nodweddu'n gywir. [28,29].
Mae nodweddu amaeth-fioamrywiaeth yn drylwyr yn enetig ac yn ffenoteipaidd er mwyn sicrhau cadwraeth briodol o adnoddau genetig planhigion a hyrwyddo'r defnydd o genoteipiau penodol yn y gadwyn werth [30-un]. Simple sequence repeat (SSR) markers have been often chosen for mapping [33-un], olion bysedd DNA a gwahaniaethu ar gyltifar [36-un], and reliable estimation of genetic variability within and among landraces [39-un], gan eu bod yn benodol i locws, yn aml-alelig, wedi'u hetifeddu'n gyffredin, yn atgynhyrchadwy iawn, ac yn addas ar gyfer genoteipio awtomataidd.
Yn yr astudiaeth bresennol, fe wnaethom ganolbwyntio ein sylw ar ras draddodiadol Apulian, yr “Acquaviva red winwnsyn” (ARO), sy'n cael ei drin yn unol â dulliau ffermio organig mewn ardal fach o dref Acquaviva delle Fonti, yn nhalaith Bari. (Apulia, De'r Eidal). Mae bylbiau'r ras hon yn fawr ac yn wastad a lliw coch ac fe'u defnyddir yn bennaf mewn ryseitiau lleol. Er i’r Swyddog Cofrestru Etholiadol ennill y nod ansawdd “Preswyliad Bwyd Araf”, gallai ei gynhyrchu gael ei hyrwyddo a’i ddiogelu ymhellach gan nodau ansawdd yr Undeb Ewropeaidd megis dynodiad daearyddol gwarchodedig (PGI) a dynodiad tarddiad gwarchodedig (POD), gan y gallai’r rhain gyfrannu at gyfyngu ar y twyll masnachol a gwella incwm tyddynwyr. Yma, defnyddiwyd marcwyr moleciwlaidd SSR fel offer pwerus i asesu amrywiad genetig ymhlith poblogaethau ARO ac i wahaniaethu ar y tir hwn o ddwy dirras nionyn coch arall yn Ne'r Eidal. At hynny, gwnaethom amcangyfrif prydlondeb a chynnwys solet hydawdd er mwyn gwerthuso blas ARO mewn perthynas â galw'r farchnad.
Canlyniadau
Sefydlu Casgliad Germplasm Nionyn Coch Acquaviva a Nodweddu Morffolegol
Defnyddiwyd hadau 13 o boblogaethau'r ras tir ARO, a roddwyd gan ffermwyr fel rhan o fframwaith y prosiect BiodiverSO Apulia Region i sefydlu casgliad germplasmau ARO.
Morphological descriptors, related to bulb, skin, and flesh were collected on ARO germplasm and on three onion landraces, two belonging to the “Tropea red onion” (TRO) landrace and one to the “Montoro copper onion” (MCO) landrace (Figure 1). Roedd yr holl fylbiau ARO yn wastad ac wedi'u nodweddu gan groen allanol coch a chnawd gyda gwahanol arlliwiau o goch. Mewn cyferbyniad, roedd cnawd bylbiau TRO yn gwbl goch, tra bod cnawd bylbiau MCO wedi'i pigmentu'n wael (Tabl S1). Caniatawyd dadansoddiad biocemegol i werthuso'r cynnwys hydawdd solet a'r prydlondeb. Fel yr adroddwyd yn Nhabl 1, gwerthoedd cymedrig cynnwys solet hydawdd bylbiau mewn poblogaethau ARO oedd 7.60, ac roedd yn amrywio o 6.00 (ARO12) i 9.50° Brix (ARO11 ac ARO13). Roedd y gwerth hwn yn uwch na'r un a amcangyfrifwyd ar gyfer y tirluniau TRO a MCO (4.25 a 6.00 ° Brix, yn y drefn honno).

Tabl 1. Cynnwys Solid Toddadwy a Gwerthoedd Peidio a Aseswyd yn Poblogaethau “Acquaviva Red Onion” (ARO), “Tropea Red Onion” (TRO), a “Montoro Copper Onion” (MCO) *.
| COD | Cynnwys Solid Hydawdd (Brix) | Pungency (pmolg-1 FW) | ||
| Cymedrig | CV y (%) | Cymedrig | CV y (%) | |
| ARO1 | 6.25 D * | 5.65 | 5.84 ab * | 23.78 |
| ARO2 | 7.25 DC | 4.87 | 6.51 y | 22.98 |
| ARO3 | 7.50 BCD | 9.42 | 5.28ab | 22.88 |
| ARO4 | 7.50 BCD | 0.00 | 6.97 y | 3.74 |
| AR 5 | 7.50 BCD | 0.00 | 6.80 y | 9.68 |
| ARO6 | 6.25 D | 5.65 | 4.51ab | 39.18 |
| ARO7 | 7.25 DC | 4.87 | 5.25ab | 15.44 |
| ARO8 | 9.00 AB | 0.00 | 7.04 y | 3.49 |
| ARO9 | 8.25 ABC | 4.28 | 6.84 y | 0.15 |
| ARO10 | 7.00 DC | 0.00 | 5.94ab | 6.57 |
| ARO11 | 9.50 Mae | 7.44 | 5.54ab | 16.43 |
| ARO12 | 6.00 D | 0.00 | 4.91ab | 9.70 |
| ARO13 | 9.50 Mae | 7.44 | 6.63 y | 24.93 |
| MCO | 6.00 D | 0.00 | 4.18ab | 2.66 |
| TRO1 | 4.25 E | 8.31 | 2.80 b | 2.10 |
| TRO2 | 4.25 E | 8.31 | 4.28ab | 4.79 |
* Nid yw modd gyda'r un llythrennau mewn llythrennau mawr neu fach yn ystadegol wahanol ar 0.01P neu 0.05P, yn y drefn honno (Prawf SNK). y Cyfernod amrywiad.
Gwerth cymedrig pungency ARO, a aseswyd trwy gyfrwng cynnwys asid pyruvic, oedd 6.00, yn amrywio o 4.51 pmol g-1 FW (ARO6) to 7.04 (ARO8). This value was higher than the one estimated in TRO and MCO landraces (3.54 pmol g-1 FW and 4.18 pmol g-1 FW, respectively).
SSR Polymorphism and Genetic Relationships among Accessions
Yn yr astudiaeth bresennol, roedd 11 allan o 37 o gyfuniadau paent preimio SSR a brofwyd yn darparu amryffurfedd un locws, hy, gan roi dau gynnyrch mwyhau ar y mwyaf mewn un unigolyn. Yn gyffredinol, canfuwyd 55 o alelau mewn 320 o unigolion gyda nifer o alelau fesul locws yn amrywio o 2 (ACM147 ac ACM 504) i 11 (ACM132) a gwerth cymedrig o 5 alel (Tabl 2). Mewn poblogaethau unigol, roedd nifer yr alelau (Na) yn amrywio o 1.94 (ACM147 ac ACM504) i 5.38 (ACM132), tra bod nifer effeithiol yr alelau (Ne) yn amrywio o 1.41 (ACM152) i 2.82 (ACM449). Anghysonderau rhwng Na ac Ne roedd gwerthoedd oherwydd presenoldeb alelau ag amledd isel yn y poblogaethau a goruchafiaeth dim ond ychydig o alelau. Amlygwyd y gwerth heterosygosity (Ho) uchaf a arsylwyd ar gyfer ACM138 ac ACM449 (0.62), tra bod yr un isaf yn gysylltiedig ag ACM152 (0.25). Roedd heterosygosity disgwyliedig (He), sy'n cyfateb i'r disgwyliad damcaniaethol mewn poblogaeth panmictig, yn amrywio o 0.37 (ACM504) i 0.61 (ACM132, ACM138, ac ACM449). Roedd mynegai sefydlogi Wright (Fis), yn dangos gwerthoedd yn agos at sero (cyfartaledd o 0.05) ar gyfer yr holl farcwyr, gan nodi gwerthoedd tebyg rhwng lefelau heterosygosity a welwyd a'r lefelau heterosygosity disgwyliedig, fel y disgwyliwyd ar gyfer rhywogaeth sy'n croesi. Amcangyfrifwyd effeithlonrwydd marciwr SSR unigol mewn olion bysedd genetig gan y mynegai cynnwys gwybodaeth polymorffig (PIC), gyda gwerth cymedrig o 0.48 ac yn amrywio o 0.33 (ACM504) i 0.67 (ACM132). Roedd mynegai effeithlonrwydd arall, Mynegai Gwybodaeth Shannon (I) yn dangos gwerth cymedrig o 0.84, ac roedd y gwerthoedd tybiedig yn amrywio o 0.45 (ACM152) i 1.20 (ACM132).
Tabl 2. Amryffurfedd Nodweddion yr 11 Marciwr SSR a Ddefnyddir i Amcangyfrif Amrywiaeth Genetig mewn Poblogaethau ARO, TRO, ac MCO. Cyfanswm Nifer yr Alelau (Na), Ystod Maint Bandiau, a Mynegai Cynnwys Gwybodaeth Polymorffig (PIC) Cyfeiriwch at y Set Gyfan o 320 o Unigolion a Genoteipiwyd yn yr Astudiaeth hon. Nifer yr Alelau (Na), nifer yr Alelau Effeithiol (Ne), Heterosygosedd Arsylwi (Ho), Heterosygosity Disgwyliedig (He), Mynegai Gosodiad (Fis), ac mae Mynegai Gwybodaeth Shannon (I) yn cyfeirio at Werthoedd Cymedrig a Gyfrifwyd o 16 o Boblogaethau, Pob un wedi'i Gyfansoddi gan 20 o Unigolion.
| Locus. | Cyfanswm Na | Size Range (bp) | PIC | Cymedrig | |||||
| Na | Ne | Ho | He | I | Fis | ||||
| ACM91 | 4 | 189-205 | 0.40 | 2.63 | 1.72 | 0.38 | 0.39 | 0.66 | 0.04 |
| ACM101 | 4 | 229-241 | 0.52 | 2.94 | 2.37 | 0.53 | 0.56 | 0.92 | 0.06 |
| ACM132 | 11 | 186-248 | 0.67 | 5.38 | 2.78 | 0.55 | 0.61 | 1.20 | 0.09 |
| ACM138 | 5 | 242-272 | 0.66 | 3.69 | 2.82 | 0.62 | 0.61 | 1.09 | 0.02- |
| ACM147 | 2 | 264-266 | 0.37 | 1.94 | 1.83 | 0.44 | 0.44 | 0.62 | 0.01- |
| ACM152 | 4 | 228-244 | 0.25 | 2.38 | 1.41 | 0.25 | 0.27 | 0.45 | 0.07 |
| ACM235 | 4 | 286-298 | 0.41 | 2.81 | 1.77 | 0.44 | 0.41 | 0.72 | 0.06- |
| ACM446 | 6 | 108-120 | 0.56 | 3.50 | 2.48 | 0.49 | 0.58 | 1.01 | 0.16 |
| ACM449 | 8 | 120-140 | 0.66 | 4.88 | 2.82 | 0.62 | 0.61 | 1.18 | 0.03- |
| ACM463 | 5 | 202-210 | 0.47 | 3.38 | 1.95 | 0.46 | 0.48 | 0.83 | 0.05 |
| ACM504 | 2 | 188-192 | 0.33 | 1.94 | 1.64 | 0.30 | 0.37 | 0.54 | 0.20 |
| Cymedrig | 5 | 0.48 | 3.22 | 2.15 | 0.46 | 0.48 | 0.84 | 0.05 |
Ymhlith y poblogaethau, dangosodd ARO3, ARO6, ARO8, ARO10, TRO1, ac MCO lefel uchel o amrywiad genetig (Ho > 0.5), tra gwelwyd yr amrywiaeth isaf yn y boblogaeth ARO7 (Ho = 0.27) (Tabl Atodol S2). Yn gyffredinol, dangosodd yr holl dderbyniadau Fis gwerthoedd yn agos at sero (Fis gwerth cymedrig = 0.054), fel y disgwylir o dan amodau paru ar hap.
Analysis of Molecular Variance and Genetic Structure
Cafodd rhaniad hierarchaidd amrywiad genetig ymhlith ac o fewn poblogaethau ei gyfrifo gan AMOVA. Amlygodd y canlyniadau ffracsiwn sylweddol o amrywiad genetig o fewn poblogaethau (87%). Roedd yr amrywiad rhwng poblogaethau, 13%, yn arwyddocaol iawn (P < 0.001) (Tabl 3). Roedd gwerthoedd paramedr Fpt, sy'n cyfateb i fynegai gosod Fst Wright, yn amrywio o 0.002 (ARO2/ARO10) i 0.468 (ARO7/TRO2), yn arwyddocaol (P < 0.05), except for nine pairwise comparisons (Supplementary Table S3).
Tabl 3. Dadansoddiad o Amrywiant Moleciwlaidd o 320 Genoteipiau o 16 o Boblogaethau o allium cepa L.
| ffynhonnell | df | Swm y Sgwariau | Amcangyfrif Amrywiant | Amrywiant (%) | Fpt | P |
| Ymhlith poblogaethau | 15 | 458.63 | 1.16 | 13% | ||
| Within populations | 304 | 2272.99 | 7.50 | 87% | 0.134 | 0.001 |
| Cyfanswm | 319 | 2731.62 | 8.66 |
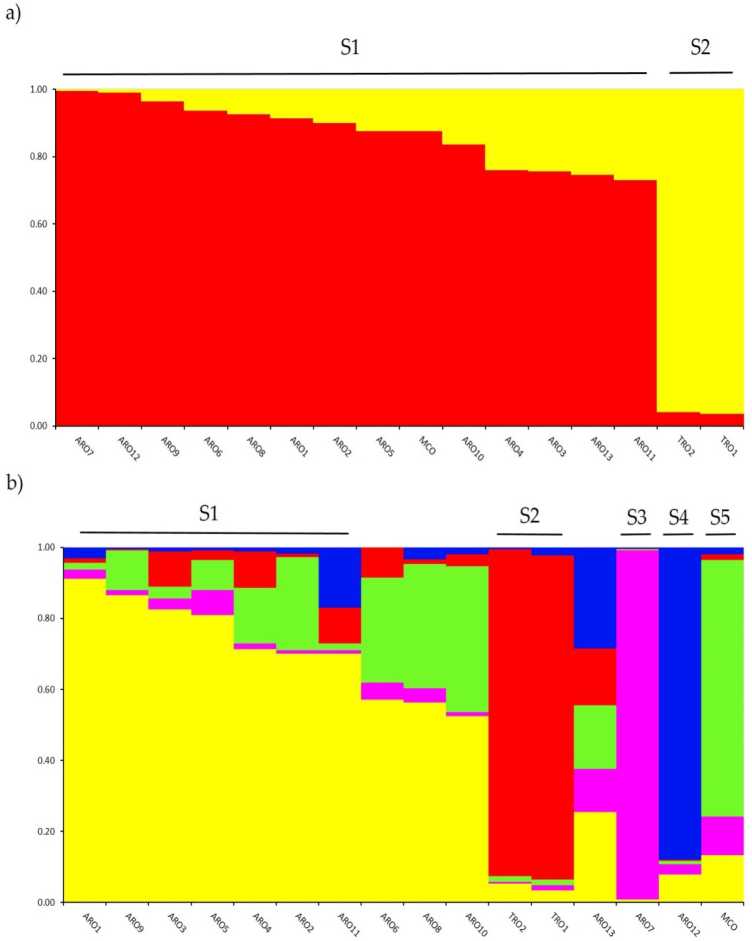
Ymchwiliad i adeiledd genetig yn y A. cepa collection genotyped in this study was performed by means of the admixture model-based clustering analysis implemented in the software STRUCTURE. The Evanno AK method suggested subdivision in two clusters (K = 2) as the most informative for our set ddata,gyda the nesaf uchaf peak yn K = 5 (sopplementaiv Rgure S1). Mae ar gyfer K = 2, ahpopulations were assigned to onaf y ddau glwstwr gyda a rnernbertoip coefficient (q) > 0.7. As shown yn Ffigur 2a, roedd y clwstwr cyntaf (a enwir S1) yn cynnwys MCO a holl boblogaethau ARO, tra bod clwstwr S2 yn grwpio'r ddwy boblogaeth GRhT. Ar K = 5, yn rhoi disgrifiad dyfnach o'r set ddata (Ffigur 2b), 75% of the accessions were assigned to one of the five cluster. Separation between ARO (S1) and TRO (S2) was confirmed, although some ARO populations were admixed (q < 0.7) or grouped separately in the two new clusters S3 and S4 (ARO7 and ARO12, respectively). Interestingly, the MCO commercial type formed a distinct cluster (S5) separated from the Apulian red onion.
Genetic Relationships among Populations
SSR polymorphism allowed to draw a dendrogram of genetic diversity and the results of the phylogenetic analysis are shown in Figure 3a. Yma, rhannwyd y casgliad germplasm yn bum grŵp a ategwyd yn gryf gan werthoedd bootstrap. Gwahanwyd poblogaethau ARO7 ac ARO12 ar unwaith oddi wrth y poblogaethau a oedd yn weddill gan ffurfio dau glwstwr gwahanol. Roedd y trydydd clwstwr yn cynnwys y ddwy boblogaeth fasnachol o TRO, ac yn y cyfamser roedd y pedwerydd nod yn rhannu MCO oddi wrth un ar ddeg o boblogaethau ARO. Ymchwiliwyd ymhellach i'r berthynas enetig sy'n digwydd ymhlith poblogaethau trwy gyfrwng prif ddadansoddiad cydgysylltu (PCoA) (Ffigur 3b). As previously highlighted, ARO populations were grouped tightly, except for ARO12 and ARO7, which appeared in isolated positions in the PCoA plot. The two TROs and the MCO populations were scattered in the lower-right panel of the plot.
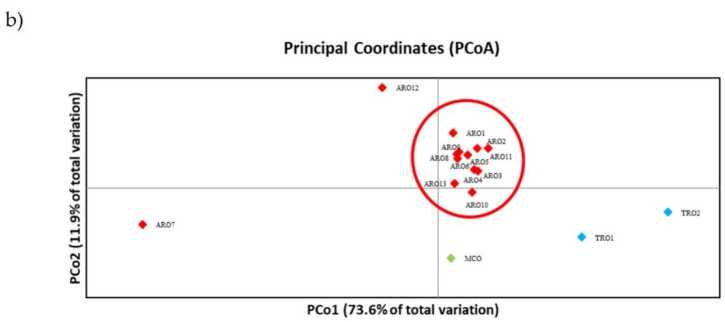
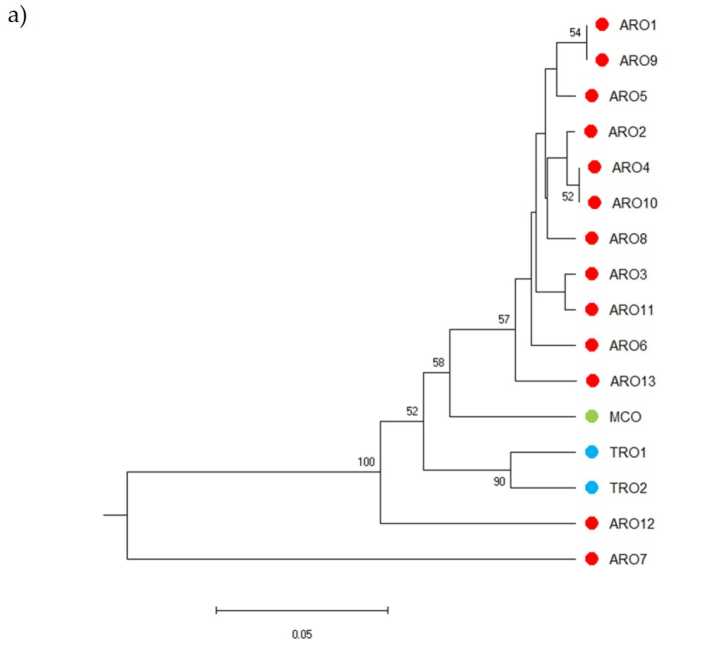
Ffigur 3. Genetic diversity among 16 A. cepa poblogaethau a nodweddir yn yr astudiaeth hon, yn seiliedig ar eu proffil SSR. (a) UPGMA dendrogram of genetic distance. Bootstrap support values >50 are indicated above the corresponding nodes; (b) principal component analysis (PCoA). The cluster circled in red fully matched with the group generated by phylogenetic analysis and constituted by 11 ARO accessions.
Trafodaeth
O fewn y swm mawr o amaeth-fioamrywiaeth sy'n cael ei drin yn draddodiadol yn Ne'r Eidal, mae tirrasys nionyn yn cynrychioli cynhyrchion arbenigol y mae angen eu cadw rhag y risg o erydiad genetig a bygythiad cyltifarau modern yn eu lle. Yn fframwaith y prosiect rhanbarthol BiodiverSO, gyda'r nod o gasglu, nodweddu, hyrwyddo a diogelu adnoddau genetig rhanbarth Apulia sydd â chysylltiad cryf â threftadaeth leol, fe wnaethom sefydlu casgliad hadau o 13 o boblogaethau'r ARO landrace. Gwnaethom adrodd ar yr asesiad cyntaf o amrywiad ARO o ran polymorphisms DNA a dau baramedr biocemegol, cynnwys solid hydawdd ac asid pyruvic, yn ymwneud â nodweddion blas ac o bwysigrwydd ar gyfer derbyn cynhyrchion ffres heb eu coginio. Yn ogystal, cymharwyd data ar y landrace ARO â'r rhai a gasglwyd ar ddau dirras nionyn pigmentog arall yr oedd yn aml yn camgymryd â hwy.
Tynnodd dadansoddiadau biocemegol sylw at felyster y 13 o boblogaethau ARO, yn ymwneud â chynnwys solet hydawdd uchel a chyflymder canolig, yn unol â chanllawiau'r diwydiant winwnsyn melys [31]. ARO bulbs were sweeter than those of the TRO and MCO landraces, and displayed a slightly higher pungency. However, sweetness in onions is due to a balance between sugar content and pungency, therefore this characterization could be useful to support the selection of genotypes of value, usually carried out by farmers only based on the morphology.
Cadarnhawyd bod marcwyr SSR yn arf defnyddiol i wahaniaethu ar genoteipiau, er eu bod wedi'u casglu o fewn ardal dyfu gul fel tref Acquaviva delle Fonti. Roedd y marcwyr a ddewiswyd yn dangos nifer uwch o alelau na'r marcwyr a nodwyd yn flaenorol [43] ac [44], ond yn is na'r marcwyr a adroddwyd gan [45]. Moreover, 50% of our set of markers showed PIC index values greater than 0.5, proving to be suitable to discriminate the populations in the collection, as suggested by [46]. Assessment of diversity within populations revealed similar values between Ho and He, resulting in low Fis gwerthoedd. Mae hyn yn cyd-fynd â natur all-groesol A. cepa, sy'n dioddef yn ddifrifol o iselder mewnfridio [47]. Mae'r Fis value calculated in onion populations considered in this study (0.054) was lower than that the one previously reported by [45] (0.22) and almost identical to the one found by [31] (0.08) a [48] (0.00) a asesodd amrywiaeth genetig mewn tirrasau nionyn o ogledd-orllewin Sbaen a Niger, yn y drefn honno. Mae lefelau nodedig o heterosygosity mewn poblogaethau ARO yn atgyfnerthu'r syniad bod Apulia yn cynrychioli canolfan amrywiaeth ar gyfer llawer o rywogaethau garddwriaethol [32, 42, 49-un].
Amlygodd AMOVA fod y rhan fwyaf o amrywiadau moleciwlaidd yn y casgliad genoteip yn yr astudiaeth hon yn gorwedd o fewn y poblogaethau. Fodd bynnag, mae gwahaniaeth genetig sylweddol rhwng poblogaethau (FPT values) revealed the occurrence of genetic stratification. In fact, although our results indicated the presence of genetic uniformity in most ARO populations, forming a well-defined cluster, the ARO7 and ARO12 populations displayed a clearly distinct genetic profile. This result could be due to a different origin of seeds used by the two farmers from which the populations were collected. Moreover, based on the results obtained, the ARO landrace can be considered clearly distinct at the genetic level from the TRO and MCO landraces. In a recent study, [29] asesu amrywiaeth genetig nifer o dirrasau nionyn Eidalaidd gan gynnwys “Acquaviva,” “Tropea,” a “Montoro.” Er i’r awduron ddefnyddio marcwyr SNP i asesu amrywiaeth genetig casgliad ehangach o winwns, nid oedd y genoteipio yn gallu gwahaniaethu “Acquaviva” o winwnsyn “Tropea” a “Montoro”. Mae'n debyg bod yr anghysondeb hwn oherwydd y gwerth PIC cymedrig isel a ddarganfuwyd (0.292), sy'n awgrymu gwybodaeth gyffredinol gymedrol o'r loci dan ddadansoddiad fel yr honnir gan [29]. Ymhellach, er mwyn ymchwilio i bresenoldeb is-strwythur yn eu clwstwr Eidalaidd, byddai wedi bod yn well dadansoddi'r genoteipiau Eidalaidd ar wahân i weddill y casgliad. Mae'n debyg y byddai wedi caniatáu delweddu patrwm amrywiaeth genetig sy'n gysylltiedig â haeniad daearyddol neu nodweddion o dan ddetholiad empirig.
I gloi, mae'r astudiaeth bresennol yn cynrychioli adroddiad cynhwysfawr ar dirras winwnsyn sy'n gysylltiedig â threftadaeth ddiwylliannol leol ac sydd o bwysigrwydd economaidd i'r ffermwyr. Mae ein canlyniadau'n amlygu, gydag ychydig eithriadau, bod ARO wedi'i nodweddu gan gronfa genynnau wedi'i diffinio'n dda, sy'n haeddu cael ei chadw rhag y risg o erydiad genetig. Felly, mae sefydlu casgliad cynrychioliadol o'r ffynhonnell werthfawr hon o amrywiaeth genetig wedi bod yn hollbwysig. Yn olaf, gallai nodweddu genetig a ffenoteipaidd yr ARO fod yn ddefnyddiol i gael marciau ansawdd gan yr Undeb Ewropeaidd.
Deunyddiau a Dulliau
Germplasm Collection, Plant Material, and DNA Extraction
A set of 13 populations of the ARO landrace were acquired within the framework of an Apulia Region project (BiodiverSO: https://www.biodiversitapuglia.it/), through a series of missions carried out in “Acquaviva delle Fonti”, a small Apulian town in Province of Bari, Italy. Collection sites of each accessions were mapped through the Geographic Information System (GIS) and reported in Table 4. In addition, two populations from the TRO landrace and one population from the MCO landrace were included in the present study and used as references. All the plant material was grown in the same environmental conditions at the experimental farm “P Martucci” of the University of Bari (41° 1’22.08″ N, 16°54’25.95″ E), under protection cage to avoid cross pollination among populations and assuring intra-population pollination by means of blowflies (Lucilia caesar). Nodweddwyd yr 16 poblogaeth am nodweddion yn ymwneud â maint a siâp bwlb a lliw croen a chnawd (Tabl S1). Yn ogystal, perfformiwyd assay cynnwys hydawdd solet gan ddefnyddio reffractomedr llaw a mesurwyd pungency mewn samplau sudd winwnsyn gan ychwanegu 2,4-dinitrophenyl hydrazine (0.125% v/v in 2N of HCl) and evaluating absorbance at 420 nm, as reported by [31]. Cynhaliwyd prawf aml-amrediad Duncan a'r prawf SNK i ganfod presenoldeb gwahaniaethau sylweddol.
Tabl 4. Rhestr o'r Poblogaethau a Gasglwyd ac a Genoteipiwyd yn yr Astudiaeth Hon. Ar gyfer Pob Poblogaeth, Adroddir Cod Adnabod, Enw Lleol, Cyfesuryn GPS, a Banc Genynnau Cadw'r Hadau.
| Côd | Enw | Cyfesurynnau GPS | Banc Genynnau y |
| ARO1 | Cipolla rossa di Acquaviva | 40°54’21.708″ N 16°49’1.631” E | Di.SSPA |
| ARO2 | Cipolla rossa di Acquaviva | 40°53’14.28″ N 16°48’56.879” E | Di.SSPA |
| ARO3 | Cipolla rossa di Acquaviva | 40°54’11.304″ N 16°49’13.079” E | Di.SSPA |
| ARO4 | Cipolla rossa di Acquaviva | 40°54’3.348″ N 16°40’27.011” E | Di.SSPA |
| ARO5 | Cipolla rossa di Acquaviva | 40°51’59.76″ N 16°53’0.527” E | Di.SSPA |
| ARO6 | Cipolla rossa di Acquaviva | 40°52’48.72″ N 16°49’43.247” E | Di.SSPA |
| ARO7 | Cipolla rossa di Acquaviva | 40°53’13.47″ N 16°50’23.783” E | Di.SSPA |
| ARO8 | Cipolla rossa di Acquaviva | 40°53’18.816″ N 16°49’33.888” E | Di.SSPA |
| ARO9 | Cipolla rossa di Acquaviva | 40°54'51.372″ N 16°49'3.504" E | Di.SSPA |
| ARO10 | Cipolla rossa di Acquaviva | 40°54’1.188″ N 16°49’24.311” E | Di.SSPA |
| ARO11 | Cipolla rossa di Acquaviva | 40°52'49.8″ N 16°49'48.575" E | Di.SSPA |
| ARO12 | Cipolla rossa di Acquaviva | 40°52’38.892″ N 16°49’28.379” E | Di.SSPA |
| ARO13 | Cipolla rossa di Acquaviva | 40°53’21.768″ N 16°49’29.711” E | Di.SSPA |
| TRO1 | Cipolla rossa lunga di Tropea | - | Di.SSPA |
| TRO2 | Cipolla rossa tonda di Tropea | - | Di.SSPA |
| MCO | Cipolla ramata di Montoro | - | Di.SSPA |
| y Di.SSPA, Adran y Gwyddorau Pridd, Planhigion a Bwyd, Prifysgol Bari. |
Cafodd deunydd dail o 20 genoteip y boblogaeth ei samplu a'i storio ar -80 °C nes ei ddefnyddio. Ar gyfer rhywogaethau sy'n llawn polysacarid, fel A. cepa, mae camau cyntaf tynnu polysacarid yn hanfodol i gael DNA o ansawdd da, felly perfformiwyd golchiadau cychwynnol mewn byffer STE (0.25 M swcros, 0.03 M Tris, 0.05 M EDTA) fel y disgrifiwyd gan [52]. Total DNA was extracted following the CTAB method [53] ac yn olaf fe'i gwiriwyd am ansawdd a chrynodiad gan Nano Drop 2000 UV-vis spectrophotometer (ThermoScientific, Waltham, MA, UDA) a 0.8% electrofforesis gel agarose.
Dadansoddiad SSR
16 EST-SSR primer combinations developed by [54] ac a brofwyd yn flaenorol mewn astudiaethau amrywiaeth genetig gan [43] ac [44] a 21 SSR genomig [45-un] were screened to evaluate their suitability (Supplementary Table S4). Genotyping was performed using the economic fluorescent tagging method in which the M13 tail is added to each forward SSR primer [56]. Paratowyd cymysgeddau PCR mewn adwaith 20 gL yn cynnwys: 50 ng o gyfanswm DNA, 0.2 mM o gymysgedd dNTP, 1X o glustogiad adwaith PCR, 0.8 U o polymeras DNA DreamTaq (Thermo Scientific, Waltham, MA, UDA), 0.16 gM o breimio gwrthdro , 0.032 gM o preimiwr blaen wedi'i ymestyn gyda'r dilyniant M13 (5′-TGTAAAACGACGGCCAGT-3′), a 0.08 gM o breimiwr M13 cyffredinol wedi'i labelu â llifynnau fflwroleuol FAM neu NED (Sigma-Aldrich, St. Louis, MO, UDA). Cyflawnwyd yr adweithiau PCR yn y thermocwlydd SimpliAmp (Cymhwysol Biosystems, CA, UDA) gyda'r amodau canlynol ar gyfer mwyafrif y parau preimio: 94 ° C am 5 munud, 40 cylch ar 94 ° C am 30 s, 58 ° C am 45 s a 72 °C am 45 s a hiriad terfynol ar 72 °C am 5 munud. O ran ACM446 ac ACM449, cymhwyswyd PCR touchdown gydag anelio o 60 ° C i 55 ° C dros 10 cylch, 30 cylch ar 55 ° C, ac yna estyniad terfynol o 5 munud ar 72 ° C. Llwythwyd cynhyrchion PCR i mewn i blât 96-ffynnon a'u cymysgu â 14 gL o Hi-Di Formamide (Life Technologies, Carlsbad, CA, UDA) a 0.5 gL GeneScan 500 ROX Size Standard (Life Technologies, Carlsbad, CA, UDA). Datryswyd amplicons trwy beiriant dilyniannu capilarïau ABI PRISM 3100 Avant Genetic Analyzer (Life Technologies, Carlsbad, CA, UDA), lle cafodd yr alelau eu sgorio fel cyd-ddominyddol a'u neilltuo trwy ddefnyddio Fersiwn Meddalwedd GeneMapper 3.7.
The softwares GenAlEx 6.5 [57] a Cervus 3.0.7 [58] eu defnyddio i amcangyfrif nifer yr alelau (Na), nifer yr alelau effeithiol (Ne), heterosygosity a arsylwyd (Ho), heterosygosedd disgwyliedig (He), cynnwys gwybodaeth amrymorffig (PIC), mynegai gwybodaeth Shannon (I), a mynegai sefydlogi (Fis). ) ar gyfer pob locws SSR.
Asesiad o Amrywiaeth Genetig
Gwerthuswyd rhaniad hierarchaidd amrywiad genetig ymhlith ac o fewn y poblogaethau nionod gan GenAlEx 6.5 [57] through the analysis of molecular variance (AMOVA) with 999 bootstrapping to test for significance. Moreover, GenAlEx 6.5 software was used to estimate the diversity within each population by computing the average of Ho, He, and Fis over all the SSR loci.
Cafodd strwythur poblogaeth ei gasglu gan yr algorithm clystyru seiliedig ar fodel Bayesaidd a weithredwyd yn y meddalwedd STRUCTURE v.2.3.4 [59]. The data set was run with a number of hypothetical clusters (K), ranging from 1 to 10, setting ten independent runs per each K value. For each run, aiming to verify the consistence of results, 100,000 initial burn-in period and 100,000 Markov Chain Monte Carlo (MCMC) iterations were performed under the admixture model and independent allele frequencies among populations. The most likely K value was determined implementing the AK method, described by [60], yn y rhaglen we STRUCTURE HARVESTER [61]. Neilltuwyd poblogaeth unigol i glwstwr penodol pan oedd ei chyfernod aelodaeth (gwerth q) yn uwch na 0.7, fel arall fe'i hystyriwyd o dras gymysg.
Principal coordinate analysis was performed in order to visualize patterns of genetic relationship among accessions revealed by the Nei’s genetic distance matrix (Supplementary Table S5). Based on allele frequencies, a dendrogram of genetic distance was constructed implementing the unweighted pair group method with arithmetic averages (UPGMA) cluster analysis in the POPTREEW software [62]. Defnyddiwyd Bootstrapping i asesu'r hyder mewn clystyru hierarchaidd, gan osod 100 o ailsamplu'r set ddata. Yn olaf, meddalwedd MEGA X [63] ei ddefnyddio fel meddalwedd tynnu coed.
Deunyddiau Atodol: Mae'r canlynol ar gael ar-lein yn http://www.mdpi.com/2223-7747/9/2/260/s1. Table S1: Morphological characterization of ARO, MCO, and TRO bulbs. Table S2: Heterozygosity and fixation indices calculated for ARO landraces and TRO and MCO landraces. Table S3: Pairwise values of the Fpt parameter. Table S4: List of the SSRs used in the study. Table S5. Pairwise population matrix of Nei genetic distance. Figure S1: Line chart of K values changing with Evanno’s Delta K.
Cyfraniadau Awdur: C.L. and L.R. conceived the study and designed the experiment; C.L. and P.I. performed molecular marker analysis; A.R.M. and V.Z. performed the field trials; R.M., S.P., G.R., and C.L. were involved in data analysis; R.M. and C.L. wrote the manuscript. All authors have read and agreed to the published version of the manuscript.
cyllid: Ariannwyd y gwaith hwn gan brosiect Rhanbarthol Apulian “Bioamrywiaeth rhywogaethau llysiau Apulian”—Programma di Sviluppo Rurale per la Puglia 2014-2020. Misura 10—Sottomisura 10.2; grant CUP H92C15000270002, yr Eidal.
Cydnabyddiaethau: Acknowledgements are due to “Azienda Agricola Iannone Anna” and “Associazione produttori della vera cipolla rossa di Acquaviva” for providing plant materials used in the experiment.
Gwrthdaro Buddiannau: Nid yw'r awduron yn datgan unrhyw wrthdaro buddiannau.
Cyfeiriadau
- 1. Stearn, WT Sawl rhywogaeth o Allium sy'n hysbys? Kew Mag. 1992, 9, 180-182. [CrossRef]
- 2. FAOSTAT. Cronfa Ddata Ystadegol FAO. Ar gael ar-lein: http://www.fao.org/2017 (accessed on 8 January 2019).
- 3. Bloc, E. Cemeg garlleg a nionyn. Sci. Yn. 1985, 252, 114-119. [CrossRef]
- 4. Lee, B. ; Jung, JH; Kim, HS Asesiad o winwnsyn coch ar weithgaredd gwrthocsidiol mewn llygod mawr. Food Chem. Toxicol. 2012, 50, 3912 3919-. [CrossRef]
- 5. Lee, SM; Lleuad, J. ; Chung, JH; Cha, YJ; Shin, MJ Effaith darnau o groen winwnsyn llawn quercetin ar thrombosis rhydwelïol mewn llygod mawr. Food Chem. Toxicol. 2013, 57, 99 105-. [CrossRef] [PubMed]
- 6. Yoshinari, O.; Shiojima, Y.; Igarashi, K. Effeithiau gwrth-ordewdra dyfyniad nionyn mewn llygod mawr brasterog diabetig zucker. Maetholion 2012, 4,1518-1526. [CrossRef]
- 7. Akash, M.S.H.; Rehman, K.; Chen, S. Spice plant Allium cepa: Dietary supplement for treatment of type 2 diabetes mellitus. Maeth 2014, 30, 1128-1137. [CrossRef] [PubMed]
- 8. Wang, Y. ; Tian, WX; Ma, XF Effeithiau Ataliol o winwnsyn (Allium cepa L.) dyfyniad ar amlhau celloedd canser ac adipocytes trwy atal synthase asid brasterog. Asian Pac. J. Cancer Prev. 2012,13, 5573 5579-. [CrossRef] [PubMed]
- 9. Lai, WW; Hsu, SC; Chueh, FS; Chen, YY; Yang, JS; Lin, YH; Lien, JC; Tsai, CH; Mae Chung, JG Quercetin yn atal mudo ac ymlediad o gelloedd canser y geg dynol SAS trwy atal llwybrau signalau NF-kappaB a matrics metalloproteinase-2/-9. Gwrthganser Res. 2013, 33, 1941-1950. [PubMed]
- 10. Nicastro, HL; Ross, SA; Milner, JA Garlleg a winwns: Eu priodweddau atal canser. Canser Cyn. Res. 2015, 8,181-189. [CrossRef]
- 11. Forte, L. ; Torricelli, P.; Boanini, E.; Gazzano, M.; Rubini, K.; Fini, M. ; Bigi, A. Priodweddau gwrthocsidiol ac atgyweirio esgyrn hydroxyapatite â swyddogaeth quercetin: Astudiaeth cyd-ddiwylliant celloedd osteoblast-osteoclast-endothelial in vitro. Biomater Acta. 2016, 32, 298 308-. [CrossRef]
- 12. Yamazaki, Y.; Iwasaki, K.; Mikami, M.; Yagihashi, A. Dosbarthiad un ar ddeg o ragflaenwyr blas, S-Alk(en)yl-L-cysteine deilliadau, mewn saith o lysiau Allium. Gwyddor Bwyd. Technol. Res. 2011, 17, 55 62-. [CrossRef]
- 13. Block, E. The organosulfur chemistry of the Genus Allium—Implications for the organic chemistry of sulphur. Angew. Cemeg. Int. Ed. Eng. 1992, 31, 1135-1178. [CrossRef]
- 14. Griffiths, G.; Trueman, L.; Crowther, T.; Thomas, B.; Smith, B. Onions-A global benefit to health. Phytother. Res. 2002,16, 603 615-. [CrossRef]
- 15. Schwimmer, S.; Weston, W.J. Enzymatic development of pyruvic acid in onion as a measure of pungency. J. Amaeth. Cemegydd Bwyd. 1961, 9, 301 304-. [CrossRef]
- 16. Ketter, CAT; Randle, WM Asesiad pungency mewn winwns. Yn Astudiaethau Profedig ar gyfer Addysgu Labordy; Karcher, S.J., Ed.; Association for Biology Laboratory Education (ABLE): New York, NY, USA, 1998; Volume 19, pp. 177-196.
- 17. Hanelt, P Taxonomy, evolution, and history. In Onions and Allied Crops, Vol. I. Botany, Physiology and Genetics; Rabinowitch, HD, Brewster, JL, Gol.; Gwasg CRC: Boca Raton, FL, UDA, 1990; tt 1-26.
- 18. Rabinowitch, HD; Currah, L. Allium Crop Science: Recent Advances; Cyhoeddi CABI: Wallingford, DU, 2002.
- 19. Mallor, C.; Carravedo, M.; Estopanan, G.; Mallor, F. Characterization of genetic resources of onion (Allium cepa L.) from Spanish secondary centre of diversity. Span. J. Agric. Res. 2011, 9, 144-155. [CrossRef]
- 20. Ferioli, F.; D’Antuono, L.F. Evaluation of phenolics and cysteine sulfoxides in local onion and shallot germplasm from Italy and Ukraine. Genet. Adnodd. Evol Cnwd. 2016, 63, 601 614-. [CrossRef]
- 21. Petropoulos, SA; Fernandes, A.; Barros, L.; Ferreira, ICFR; Ntatsi, G. Disgrifiad morffolegol, maethol a chemegol o 'vatikiotiko', ras leol nionyn o Wlad Groeg. Cemeg Bwyd. 2015,182, 156-163. [CrossRef]
- 22. Liguori, L.; Adiletta, G.; Nazzaro, F.; Fratianni, F.; Di Matteo, M.; Albanese, D. Biochemical, antioxidant properties and antimicrobial activity of different onion varieties in the Mediterranean area. J. Bwyd Mesur. Cymeriad. 2019,13, 1232-1241. [CrossRef]
- 23. Yoo, K.S.; Pike, L.; Crosby, K.; Jones, R.; Leskovar, D. Differences in onion pungency due to cultivars, growth environment, and bulb sizes. Sci. Hortig. 2006,110, 144-149. [CrossRef]
- 24. Beesk, N. ; Perner, H.; Schwarz, D.; George, E.; Kroh, LW; Rohn, S. Dosbarthiad quercetin-3, 4′-O-diglucoside, quercetin-4′-O-monoglucoside, a quercetin mewn gwahanol rannau o'r bwlb winwnsyn (Allium cepa L.) dan ddylanwad genoteip. Cemeg Bwyd. 2010,122, 566 571-. [CrossRef]
- 25. Caruso, G.; Conti, S.; Villari, G.; Borrelli, C.; Melchionna, G.; Minutolo, M.; Russo, G.; Amalfitano, C. Effects of transplanting time and plant density on yield, quality and antioxidant content of onion (Allium cepa L.) in southern Italy. Sci. Hortig. 2014,166, 111-120. [CrossRef]
- 26. Perez-Gregorio, MR; Regueiro, J.; Simal-Gandara, J.; Rodrigues, AS; Almeida, DPF Cynyddu gwerth ychwanegol winwns fel ffynhonnell flavonoidau gwrthocsidiol: Adolygiad beirniadol. Meini prawf. Parch Bwyd Sci. Maeth. 2014, 54,1050-1062. [CrossRef] [PubMed]
- 27. Pohnl, T. ; Schweiggert, RM; Carle, R. Effaith dull tyfu a dethol cyltifar ar garbohydradau hydawdd ac egwyddorion llym mewn winwns (Allium cepa L.). J. Amaeth. Cemegydd Bwyd. 2018, 66, 12827-12835. [CrossRef] [PubMed]
- 28. Tedesco, I. ; Carbone, V. ; Spagnuolo, C. ; Minasi, P.; Russo, GL Nodi a meintioli flavonoidau o ddau gyltifar deheuol Eidalaidd o allium cepa L., Tropea (nionyn coch) a Montoro (nionyn copr), a'u gallu i amddiffyn erythrocytes dynol rhag straen ocsideiddiol. J. Amaeth. Cemegydd Bwyd. 2015, 63, 5229 5238-. [CrossRef]
- 29. Villano, C.; Esposito, S.; Carucci, F.; Frusciante, L.; Carputo, D.; Aversano, R. Mae genoteipio trwybwn uchel mewn winwnsyn yn datgelu strwythur amrywiaeth genetig ac SNPs llawn gwybodaeth sy'n ddefnyddiol ar gyfer bridio moleciwlaidd. Mol. Brid. 2019, 39, 5. [CrossRef]
- 30. Mercati, F.; Longo, C. ; Poma, D.; Araniti, F.; Lupini, A.; Mammano, MM; Fiore, MC; Abenavoli, MR; Sunseri, F Amrywiad genetig o domato Eidalaidd oes silff hir (Solanum lycopersicum L.) collection by using SSR and morphological fruit traits. Genet. Adnodd. Evol Cnwd. 2014, 62, 721 732-. [CrossRef]
- 31. Gonzalez-Perez, A.S.; Mallor, C. ; Garces-Claver, A.; Merino, F.; Taboada, A. ; Rivera, A.; Pomar, F.; Perovic, D.; Silvar, C. Archwilio amrywiaeth genetig a nodweddion ansawdd mewn casgliad o winwnsyn (Allium cepa L.) landraces from north-west Spain. Geneteg 2015, 47, 885 900-. [CrossRef]
- 32. Lotti, C.; Iovieno, P.; Centomani, I.; Marcotrigiano, A.R.; Fanelli, V.; Mimiola, G.; Summo, C.; Pavan, S.; Ricciardi, L. Genetic, bio-agronomic, and nutritional characterization of kale (brassica oleracea L. var. acephala) diversity in Apulia, Southern Italy. Amrywiaeth 2018,10, 25. [CrossRef]
- 33. Bardaro, N.; Marcotrigiano, A.R.; Bracuto, V.; Mazzeo, R.; Ricciardi, F.; Lotti, C.; Pavan, S.; Ricciardi, L. Genetic analysis of resistance to Crenata Orobanche (Forsk.) mewn pys (Pisum sativum L.) low-strigolactone line. J. Pathol Planhigion. 2016, 98, 671-675.
- 34. Wako, T.; Tsukazaki, H.; Yaguchi, S.; Yamashita, K.; Ito, S.; Shigyo, M. Mapio loci nodweddion meintiol ar gyfer amser bolltio mewn sypiau winwnsyn (Allium fistulosum L.). Euphytica 2016, 209, 537 546-. [CrossRef]
- 35. Dhaka, N.; Mukhopadhyay, A.; Paritosh, K.; Gupta, V. ; Pental, D.; Pradhan, AK Nodi SSRs genig ac adeiladu map cyswllt yn seiliedig ar SSR yn Juncea bresych. Euphytica 2017, 213, 15. [CrossRef]
- 36. Anandhan, S.; Mote, SR; Gopal, J. Gwerthusiad o hunaniaeth amrywogaethol nionyn gan ddefnyddio marcwyr SSR. Seed Sci. Technol. 2014, 42, 279 285-. [CrossRef]
- 37. Mitrova, K. ; Svoboda, P.; Ovesna, J. Dewis a dilysu set farciwr ar gyfer gwahaniaethu cyltifarau nionyn o'r Weriniaeth Tsiec. Tsiec J. Genet. Brid Planhigyn. 2015, 51, 62 67-. [CrossRef]
- 38. Di Rienzo, V.; Miazzi, MM; Fanelli, V. ; Sabetta, W.; Montemurro, C. Cadw a nodweddu bioamrywiaeth germplasm olewydd Apulian. Acta Hortic. 2018,1199,1-6. [CrossRef]
- 39. Mallor, C.; Arnedo-Andres, A.; Garces-Claver, A. Assessing the genetic diversity of Spanish allium cepa tirrasys ar gyfer bridio winwnsyn gan ddefnyddio marcwyr microloeren. Sci. Hortig. 2014,170, 24-31. [CrossRef]
- 40. Rivera, A.; Mallor, C.; Garces-Claver, A.; Garcia-Ulloa, A.; Pomar, F.; Silvar, C. Assessing the genetic diversity in onion (allium cepa L.) landraces from northwest Spain and comparison with the European variability. Cnydau Hortig NZJ. 2016, 44, 103-120. [CrossRef]
- 41. De Giovanni, C.; Pavan, S.; Taranto, F.; Di Rienzo, V.; Miazzi, MM; Marcotrigiano, AR; Mangini, G. ; Montemurro, C.; Ricciardi, L.; Lotti, C. Amrywiad genetig o gasgliad germplasm byd-eang o ffacbys (Cicer arietinum L.) gan gynnwys derbyniadau Eidalaidd sydd mewn perygl o erydiad genetig. Physiol. Mol. Biol. Plants 2017, 23, 197-205. [CrossRef]
- 42. Mazzeo, R. ; Morges, A. ; Sonnante, G. ; Zuluaga, DL; Pavan, S.; Ricciardi, L.; Lotti, C. Amrywiaeth genetig yn y gynddaredd brocoli (Brassica rapa L. subsp. sylvestris (L.) Janch.) from Southern Italy. Sci. Hortig. 2019, 253, 140-146. [CrossRef]
- 43. Jakse, M. ; Martin, W.; McCallum, J.; Havey, M. Amryffurfedd niwcleotid sengl, indels, ac ailadrodd dilyniant syml ar gyfer adnabod cyltifar nionyn. J. Am. Soc. Hortig. Sci. 2005,130, 912 917-. [CrossRef]
- 44. McCallum, J.; Thomson, A.S.; Pither-Joyce, M.A.; Kenel, F. Dadansoddiad amrywiaeth genetig a datblygiad marciwr polymorphism un-niwcleotid mewn winwnsyn bwlb wedi'i drin yn seiliedig ar farcwyr ailadrodd dilyniant dilyniant tag-syml a fynegir. J. Am. Soc. Hortig. Sci. 2008,133, 810 818-. [CrossRef]
- 45. Baldwin, S.; Pither-Joyce, M.; Wright, K.; Chen, L.; McCallum, J. Development of robust genomic simple sequence repeat markers for estimation of genetic diversity within and among bulb onion (Allium cepa L.) poblogaethau. Mol. Brid. 2012, 30, 1401-1411. [CrossRef]
- 46. DeWoody, JA; Honeycutt, RL; Marcwyr Microloeren Skow, LC mewn ceirw cynffon wen. J. Hered. 1995, 86, 317-319. [CrossRef] [PubMed]
- 47. Khodadadi, M.; Hassanpanah, D. Iranian onion (Allium cepa L.) ymatebion cyltifarau i iselder mewnfridio. Appl y Byd. Sci. J. 2010,11, 426 428-.
- 48. Abdou, R.; Bakasso, Y.; Saadou, M.; Baudoin, J.P.; Hardy, O.J. Genetic diversity of Niger onions (Allium cepa L.) assessed by simple sequence repeat markers (SSR). Acta Hortic. 2016,1143, 77-90. [CrossRef]
- 49. Pavan, S. ; Lotti, C. ; Marcotrigiano, AR; Mazzeo, R.; Bardaro, N.; Bracuto, V. ; Ricciardi, F.; Taranto, F.; D'Agostino, N.; Schiavulli, A.; et al. Clwstwr genetig amlwg mewn gwygbys wedi'i drin fel y'i datgelir gan ddarganfyddiad marciwr genom-eang a genoteipio. Genom Planhigion 2017, 2017,10. [CrossRef]
- 50. Pavan, S.; Marcotrigiano, A.R.; Ciani, E.; Mazzeo, R.; Zonno, V.; Ruggieri, V.; Lotti, C.; Ricciardi, L. Genotyping-by-sequencing of a melon (Cucumis melo L.) casgliad germplasm o ganolfan eilaidd o amrywiaeth yn amlygu patrymau amrywiad genetig a nodweddion genomig gwahanol gronfeydd genynnau. BMC Genom. 2017, 18, 59. [CrossRef]
- 51. Di Rienzo, V. ; Sion, S.; Taranto, F.; D'Agostino, N.; Montemurro, C.; Fanelli, V. ; Sabetta, W.; Boucheffa, A.S.; Tamendjari, A.; Pasqualone, A. ; et al. Llif genetig ymhlith poblogaeth olewydd o fewn basn Môr y Canoldir. Cyfoed J. 2018, 6. [CrossRef]
- 52. Shepherd, L.D.; McLay, T.G. Two micro-scale protocols for the isolation of DNA from polysaccharide-rich plant tissue. J. Plant Res. 2011,124, 311 314-. [CrossRef]
- 53. Doyle, JJ; Doyle, JL Ynysu DNA planhigion o feinwe ffres. Ffocws 1990,12, 13-14.
- 54. Kuhl, J.C.; Cheung, F.; Qiaoping, Y.; Martin, W.; Zewdie, Y.; McCallum, J.; Catanach, A.; Rutherford, P.; Sink, K.C.; Jenderek, M.; et al. A unique set of 11,008 onion expressed sequence tags reveals expressed sequence and genomic differences between the monocot orders asparagales and poales. Cell planhigyn 2004,16, 114 125-. [CrossRef]
- 55. Kim, H.J.; Lee, H.R.; Hyun, J.Y.; Song, K.H.; Kim, K.H.; Kim, J.E.; Hur, C.G.; Harn, C.H. Marker development for onion genetic purity testing using SSR Finder. Corëeg J. Brid. Sci. 2012, 44, 421 432-. [CrossRef]
- 56. Schuelke, M. Dull economaidd ar gyfer labelu fflwroleuol darnau PCR. Nat. Biotechnol. 2000, 18, 233 234-. [CrossRef] [PubMed]
- 57. Peakall, R. ; Smouse, PE GenAlEx 6.5: Dadansoddiad genetig yn Excel. Meddalwedd genetig poblogaeth ar gyfer addysgu ac ymchwil: Diweddariad. Biowybodeg 2012, 28, 2537 2539-. [CrossRef] [PubMed]
- 58. Kalinowski, S.T.; Taper, M.L.; Marshall, T.C. Revising how the computer program CERVUS accommodates genotyping error increases success in paternity assignment. Mol. Ecol. 2007,16, 1099-1106. [CrossRef]
- 59. Pritchard, J.K.; Stephens, M.; Rosenberg, N.A.; Donnelly, P. Association mapping in structured populations. Am. J. Hum. Genet. 2000, 67, 170-181. [CrossRef]
- 60. Evanno, G.; Regnaut, S.; Goudet, J. Detecting the number of clusters of individuals using the software STRUCTURE: A simulation study. Mol. Ecol. 2005,14, 2611 2620-. [CrossRef]
- 61. Iarll, D. ; VonHoldt, B. CYNAEAF STRWYTHUR: Gwefan a rhaglen ar gyfer delweddu allbwn STRWYTHUR a gweithredu dull Evanno. Conserv. Genet. Resour. 2011, 4. [CrossRef]
- 62. Takezaki, N.; Nei, M.; Tamura, K. POPTREEW: Web version of POPTREE for constructing population trees from allele frequency data and computing some other quantities. Mol. Biol. Evol. 2014, 31, 1622-1624. [CrossRef]
- 63. Kumar, A.S.; Stecher, G. ; Li, M. ; Knyaz, C. ; Tamura, K. MEGA X. Dadansoddiad Geneteg Esblygiadol Moleciwlaidd ar draws llwyfannau cyfrifiadura. Mol. Biol. Evol. 2018, 35, 1547-1549. [CrossRef]